武汉新病毒的扩散牵动着海外华人的心。连我们的文学城也被戏称传染了新型肺炎。
我们关心包括毒源、宿主、传染能力、传播速度、如何防御和治疗等等。
科学家也同样关心,这里回顾一下在这几天里有什么科研新进展。
一、
传染病的传播和草原或森林的火灾扩散相似,都有数学模型,可以用计算机进行模拟。数学模型有简单的,也有复杂的。所涉及的数学包括常微分方程、偏微分方程、网络动力学和分形(fractal)等。
厦门大学公共卫生学院陈田木等六人在“生物预印本网站”(biorxiv.org)发表了“模拟武汉新型冠状病毒传播的数学模型”的文章,DOI: 10.1101/2020.01.19.911669。
作者提出可以用 Reservoir-People 传播(传染)网络模型(RP模型)计算出基本繁殖数(R0),以评估新病毒的传播能力,见下图。
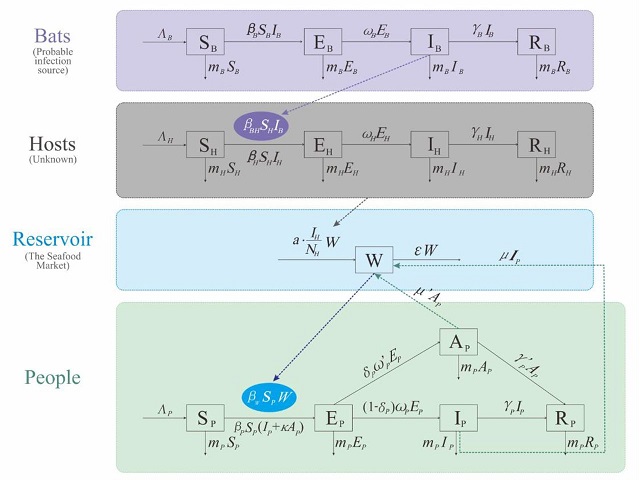
图中的第一行是病毒源,假定是蝙蝠,分为四个部分:易受感染的蝙蝠(SB),暴露的蝙蝠(EB),受感染的蝙蝠(IB)和已康复的蝙蝠(RB)。
第二行是中间宿主,也分为四个部分:易受感染的宿主(SH),暴露的宿主(EH),受感染的宿主(IH)和已康复的宿主(RH)。
第三行是传染地-海鲜市场。
第四行是人群,分为五个部分:易感人群(SP),暴露人群(EP),有症状感染者(IP),无症状感染者(AP)和康复者/死亡者(RP)。
文章给出了这14部分的微分方程。
可惜我没看到大家最关心的用此模型算出的数字。
二、
目前除复旦大学上传到美国国立卫生研究院网站上以外,到写稿时为止还有25个病毒基因序列已上传到德国的gisaid.org网站上,供专业人员下载研究。其中包括浙江疾控中心2例、中科院武汉病毒所5例、中国疾控中心病毒所3例、北京协和医学院5例、湖北疾控中心1例、广东疾控中心6例;此外还有泰国2例、日本1例。
香港城市大学董宁等人的“基因组和蛋白质结构建模分析描述2019-nCoV的起源和传染性”,DOI: 10.1101/2020.01.20.913368
文章的文摘部分说:新病毒是蝙蝠样病毒的新型,并且在基因上与人类SARS冠状病毒的距离相当远(genetically fairly distant)。对这种新病毒的刺突(S)蛋白的结构分析表明,其S蛋白仅与人细胞上的ACE2受体弱结合,而人SARS冠状病毒对ACE2受体表现出强烈的亲和力。这些发现表明,这种新病毒在人与人之间不易传播,并且理论上不应该引起严重的人类感染。
诶呀妈呀,不易传播?还是读者自己下载看看吧,如果你想接着看的话。在网上输入文章题目后面的DOI号码就可以免费下载全文。
三、
迈克尔·C·莱科(Michael C Letko)二人的“谱系B的β冠状病毒包括2019-nCoV的细胞进入和受体使用的功能评估”,DOI: 10.1101/2020.01.22.915660
文章说:β冠状病毒中分为四个谱系:谱系B(包括SARS-CoV)和新兴的2019-nCoV,具有大约200种已发布的病毒序列,而谱系C(包括MERS-CoV)具有500多个病毒序列。冠状病毒的结构研究表明,刺突RBD能够独立于其余刺突蛋白折叠,并包含与宿主受体结合的所有结构信息。
这篇也是根据已发表的RNA序列研究新病毒与人体ACE2受体结合的理论文章。说明此次事件与2003年不同的是,中国在最短的时间里公开发布了大量的病毒全基因序列,无声的与世界各国科学家合作攻关。
四、
中国科学院武汉病毒所石正丽等29人有关新型冠状病毒及其潜在的蝙蝠起源的文章,DOI: 10.1101/2020.01.22.914952。
本城博友已有介绍,这里就省略了。
五、
北大等五个单位的研究人员在《医学病毒学杂志》(Journal of Medical Virology)上在线发表了关于蛇可能是中间宿主的论文(10.1002/jmv.25682)。
各大媒体如CNN、CBS的都报道了该论文的观点,科技媒体如《科学美国人》等也有报道。
尽管文章的内容也引起了争议,但立题是对的:“谁吃了蝙蝠染上了病毒,后又与人有接触”。就像17年前SARS时:果子狸猎杀蝙蝠带了毒、然后被抓、带到市场又传染给人。只是不知道武汉的那个市场里是不是卖那两种蛇和其他几种动物,是否已取样。
该文对比了(见下图)舟山蝙蝠病毒、武汉新病毒、银环蛇、眼镜蛇、旱獭属、刺猬、穿山甲、中华菊头蝠、原鸡、智人的基因。得出了蛇最可能是中间宿主。下图取自该论文,版权:《医学病毒学》杂志。

该期刊是小开本,表格的排版很难阅读。
复旦大学卢洪洲等三人的文章“中国武汉市病因不明的肺炎暴发:神秘与奇迹”(/jmv.25678)中有句话:“上个月,大多数患者去了武汉的鱼类和野生动物市场。 这个鱼类和野生动物市场也出售活体动物,例如家禽,蝙蝠,土拨鼠和蛇”。只知道关岛人吃蝙蝠,难道国人也吃蝙蝠?
《自然》、《科学》等要经过同行评审的期刊还没有见到关于新病毒的研究文章。
六、
许多人关心新病毒的基因突变,可以到这个网站看看:https://nextstrain.org/ncov?m=num_date。这是使用来自GISAID(截止到写稿时)的数据绘制的的新型冠状病毒(nCoV)的基因组流行病学树。将鼠标移到一个端点上,就可以看到这个基因序列中哪里发生了突变。只可惜两个相邻的端点是不是有亲属关系?不知道。
